DNS-replikáció
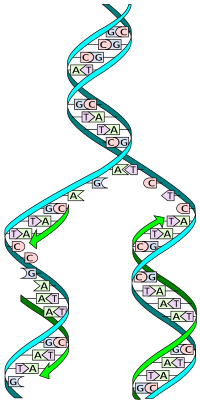
A DNS-replikáció vagy DNS-másolás az a folyamat, aminek eredményeképpen az eredeti dezoxiribonukleinsav alapján két, egymással azonos molekula keletkezik. A DNS-replikáció minden élőlényben lezajlik, ez az öröklődés alapját biztosító biológiai folyamat. A DNS két szálból áll, ezek a másolás során szétválnak és rajtuk, bázissorrendjüket templátnak használva enzimek új, komplementer (kiegészítő) szálat szintetizálnak. Ez az úgynevezett szemikonzervatív modell, amikor az utódmolekulák félig a kiindulási DNS-ből állnak. A másolás pontosságát szintén enzimek ellenőrzik.[1][2]
A sejten belül a replikáció nem a DNS-molekula végén, hanem bizonyos köztes pontokon, az origókban kezdődik.[3] A szétcsavarodó szálak és a rajtuk szintetizálódó új fonalak hozzák létre a replikációs villát. Az új szál szintézisét a DNS-polimeráz enzim végzi.
A DNS-replikáció kémcsőben, sejten kívül is elvégezhető. Ismert szekvenciájú DNS-mintát enzimek és szükséges vegyületek hozzáadásával sokszorosan le lehet másolni, ez szolgál alapul a polimeráz-láncreakció metodikájának, amelyet általánosan használnak kórokozók detektálására, az igazságügyi orvostanban, a kutatásban és egyéb területeken
A DNS szerkezete
[szerkesztés]A DNS többnyire kettős szálú struktúrába rendeződik, ahol a szálak egymás köré csavarodnak, ez az ún. kettős hélix. Az egyes szálak egymás után sorakozó nukleotidokból állnak. A nukleotidok egy dezoxiribóz cukormolekulából, egy foszfátcsoportból és egy nukleobázisból tevődnek össze. A DNS-ben négyféle nukleotid lehet, a nukleobázisuk alapján: az adenozin (bázisa az adenin), citidin (citozin), guanozin (guanin) és timidin (timin), melyeknek általánosan elterjedt rövidítése az A, C, G és T. Az adenin és a guanin purinbázis, míg a citozin és a timin pirimidin. A nukleotidok foszfát és cukorcsoportjai egymáshoz kapcsolódva alkotják a DNS-szál gerincét, amelyről oldalt lelógnak a bázisok. Két szál bázisai egymással hidrogénkötéseket tudnak létesíteni, bázispárokat hozva létre. Az adenin csak timinnel (két hidrogénkötés), míg a guanin csak citozinnal (három hidrogénkötés, ezért ez erősebb mint az A-T pár) képes összekapcsolódni. Emiatt a szétválasztott szálak egymás kiegészítői (komplementerei) és bármelyik alapul szolgálhat a másik szál szintéziséhez (egymás templátjai).
A DNS-szálaknak irányultsága van. A nukleotidok dezoxiribózához két foszfátcsoport kapcsolódik, egyik a 3., a másik az 5. szénatomhoz. Aszerint, hogy melyik foszfát van közelebb a végéhez, beszélünk 3' és 5' végről. A DNS másolása, leolvasása a biológiai rendszerekben mindig 5'->3' irányban történik, ezért a nukleotidok egymásutánját, szekvenciáját is ebben az irányban adják meg. A DNS két szála fordított irányultságú, egyikük 5'-3', míg a másik 3'-5' irányban áll.[4]
A DNS-polimeráz
[szerkesztés]
A DNS-polimeráz nem egy konkrét enzim, hanem egy enzimcsalád, mely tagjainak feladata a DNS másolása.[6] Ők maguk nem képesek új szál szintézisét elkezdeni a régin, hanem csak a meglévő második szálat tudják hosszabbítani, ezért a kezdéshez egy rövid, egyszálú DNS-re vagy RNS-re, az úgynevezett primerre (ejtsd prájmer) van szükségük, amely a templáthoz kapcsolódva kis szakaszon kétszálú szerkezetet hoz létre, amelyet az enzim hosszabbíthat.
Az enzim az új DNS-szál 3' végéhez foszfodiészter kötéssel kapcsol új nukleotidokat, a régi szál bázissorrendjének megfelelően. Ehhez nukleozid-trifoszfátokat használ fel amelyekben a bázishoz és cukorhoz három foszfátcsoport csatlakozik nagyenergiájú kötéssel. Az enzim erről lehasít egy pirofoszfátot és a felszabaduló energia felhasználásával létrehozza a foszfodiészter kötést a keletkező nukleotid (nukleotid a bázis-cukor-foszfát hármas elnevezése) foszfátcsoportja és a DNS-szál 3' végének dezoxiribóza között. A felbomló nagyenergiájú kötés miatt a reakció gyakorlatilag irreverzibilis.
A DNS-polimeráz igen pontosan dolgozik, alapműködése során csak minden tízmilliomodik bázisnál téved.[7] Emellett azonban hibaészlelő és -javító aktivitással is rendelkezik: a szál végéről eltávolítja az észlelt hibás nukleotidot, majd folytatja annak hosszabbítását. Ezenkívül a replikáció után egy másik javítómechanizmus is leellenőrzi a másolás hűségét és képes különbséget tenni a régi és az újonnan készült szál között. Összességében a DNS-replikáció hibarátája mindössze egy tévedés minden egymilliárd beépített bázisban.[7]
Az élő sejtben zajló DNS-replikáció sebességét E. coli baktériumot fertőző T4 fág esetében határozták meg először.[8] A vírus DNS-polimeráza 749 nukleotidot épített be másodpercenként és ennek során minden százhetvenmilliomodiknál ejtett hibát.[9] A DNS másolása meglepően gyorsnak és pontosnak tekinthető.
A replikáció folyamata
[szerkesztés]A replikáció három fázisból áll: kezdés (iniciáció), szálhosszabbítás (elongáció) és befejezés (termináció).
Iniciáció
[szerkesztés]
A sejt osztódása előtt annak DNS-tartalma megkettőződik.[10] A folyamat bizonyos pontokon, az ún. replikációs origóknál indul, amelyekhez hozzákötődnek az iniciátor fehérjék.[3] Escherichia coli esetében az iniciátor a DnaA, míg élesztőben az origófelismerő komplex.[11] Az iniciátorok által felismert régiók többnyire A és T bázisokban gazdagok, mert két hidrogénkötésüket könnyebb felbontani, mint a G és C három kötését.[12] Ha sikeresen megkötötték a DNS-t, egyéb proteinek segítségével létrehozzák a pre-replikációs komplexet, amely szétcsavarja a DNS egymás köré tekeredő szálait és ún. replikációs buborék keletkezik.
Elongáció
[szerkesztés]A DNS-polimeráznak egy szabad 3' OH-csoportra van szüksége a feladata elvégzéséhez, vagyis az új szál 5'-3' irányban készül és ennek megfelelően a templátszálon 3'-5' irányban halad a másolóenzim. A szintézis mechanizmusát illetően négy változat ismert:
- valamennyi sejtes organizmus és sok DNS-vírus, bakteriofág és plazmid azt a módszert alkalmazza, hogy a primáz enzim egy rövid RNS-primert készít az egyszálú DNS-re, melynek szabad 3' OH-csoportjáról a DNS-polimeráz már képes elindulni.
- a retrovírusok és retrotranszpozonok egy transzfer RNS-t használnak primerként a reverz transzkriptáz számára
- az adenovírusok és a bakteriofágok φ29 családja esetében a szabad OH-csoportot egy DNS-kötő fehérje egyik aminosava szolgáltatja, ehhez kapcsolja a DNS-polimeráz az új szálat.
- az egyszálú DNS-vírusok (circovírusok, geminivírusok, parvovírusok stb.) és azok a kétszálú fágok és plazmidok amelyek a másolás guruló kör modelljét használják, a cirkuláris DNS egyik szálát (vagy ha egyszálú akkor azt) egy endonukleázzal elvágják, a nukleáz megköti az 5' véget, míg a szabad 3' végen elkezdődhet a szálhosszabbítás.
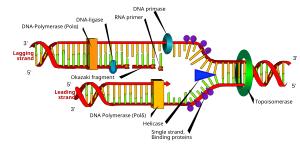
Ezek közül az első a messze legelterjedtebb és legjobban feltárt mechanizmus. Ennek során, miután a dupla hélix két szála elvált egymástól, a primáz enzim RNS-primert készít rajtuk. A vezető szálon (lásd lejjebb) egy primer készül, melyet folyamatosan, hosszasan hosszabbít meg a DNS-polimeráz, míg a követő szálra több primer szintetizálódik, melyek a következő primerig egészülnek ki, így jönnek létre az Okazaki-fragmentumok. A primerek egy RNáz távolítja el, és a helyükön maradó réseket egy másik DNS-polimeráz (nem az, amelyik a szálhosszabbítást végzi) betölti. Ez nem képes kovalensen összekötni az általa szintetizált rövid DNS-szakaszt a korábban készült hosszú szállal, ezt a feladatot a ligáz enzim látja el, amely révén a replikáció befejeződik és végeredményül hosszú, folyamatos, kétszálú DNS jön létre.
A baktériumok és eukarióták/archeák által használt primáz jelentősen különbözik egymástól. A bakteriális primáz a DnaG családba tartozik, szerkezetileg a topoizomeráz Ia és II, egyes nukleázok és DNS-javító enzimek rokona. Az eukarióta primáz viszont egészen más szerkezetű, leginkább a vírusok RNS-függő RNS-polimerázára, a reverz transzkriptázra, a ciklikus nukleotidokat készítő ciklázra és egyes DNS-polimerázokra hasonlít.[13]
A DNS replikációját többféle polimeráz végzi. E. coliban a gyors működésű DNS-polimeráz III (Pol III) végzi a szálhosszabbítást, míg a DNS-polimeráz I (Pol I) feladata az RNS-primerek lebontása és helyének DNS-sel való betöltése. A Pol I lassan (jóval lassabban, mint a Pol III) végighalad az RNS-DNS hibriden, maga előtt bontja az RNS-t, maga mögött pedig annak helyére dezoxiribóz-tartalmú nukleotidokat épít be. Eukariótákban a lassú Pol α segít a replikáció beindításában, míg a gyors szálhosszabbítók a Pol δ és Pol ε enzimek.
A DNS-szintézis előrehaladtával a buborék két oldalán folytatódik az eredeti kettős hélix szétcsavarása és mindkét végen ún. replikációs villa halad. A baktériumok kör alakú genomjában csak egy origó található és az előrehaladó replikációs formációt théta-struktúrának nevezik (a görög θ betű nyomán, amire alakja emlékeztet). Ezzel ellentétben az eukarióták kromoszómái lineárisak és rajtuk több replkációs origó is található.[14]
A replikációs villa
[szerkesztés]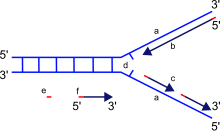
a: templát, b: vezető szál, c: követő szál, d: replikációs villa, e: primer, f: Okazaki-fragmentumok
Ahogyan a helikázok széttekerik a DNS két szálát és rajtuk folyik az új szálak szintézise, kétágú alakzat jön létre, a replikációs villa. Az egyik ág a vezető szál, a másik pedig a követő szál. Mivel a DNS-szintézis csak 5'-3' irányba történhet és a szálak egymással ellentétes orientációjúak, valahogyan meg kell oldani a fordított állású lánc replikációját.
A vezető szál annak a DNS-láncnak a neve, amelyen a replikáció iránya egybeesik a replikációs villa haladásának (vagyis a kettős hélix széttekerésének) irányával. A polimeráz ezen a szálon folyamatosan tudja olvasni a templátot és annak alapján megszakítás nélkül hosszabbítja az új láncot. Az enzim prokariótákban a Pol III, élesztőben pedig feltehetően a Pol ε.[7][15] Emberi sejtekben a vezető szál polimeráza a Pol ε, a követő szálé a Pol δ, a mitokondriumokban pedig a Pol γ[16] A Pol ε szükség esetén helyettesíteni tudja a Pol δ-t.[17]
A követő szál az, amelyiken a szintézis iránya ellentétes a replikációs villa haladásával. Ezért itt az új szál rövid szakaszokban, úgynevezett Okazaki-fragmentumokban készül. A replikáció ugyanúgy rövid RNS-primerrel kezdődik, amit később eltávolítanak és a fragmentumokat a ligázok összekapcsolják. Az Okazaki-fragmentumok baktériumokban 1000-2000 bázis, míg eukariótákban csak 100-200 bázis hosszúságúak.
Eukariótákban a primáz a Pol α enzimkomplex része.[18] A fragmentumok hosszabbítását a Pol III (prokariótákban) vagy a Pol δ/Pol ε (eukariótákban) végzi. Az RNS-primert eukarióta sejtekben szintén a Pol δ távolítja el.[19] Baktériumokban az utóbbit a Pol I végzi.
Amikor a helikáz szétcsavarja a kétszálú DNS-t, az előtte lévő hélix-szakasz forogni kényszerül és rövid időn belül akkora torziós feszültség gyülemlik fel benne, ami megállítaná a replikációs villa előrehaladását.[20] Ezt elkerülendő, a topoizomeráz enzimek időnként eltörik, majd újból összekötik a dupla hélixet; sőt ezt nem csak meglévő feszültség esetén teszik meg, hanem előre negatív másodlagos struktúrába csavarják azt.
A csupasz egyszálú DNS hajlamos másodlagos struktúrákba rendeződni, amelyek zavarják a DNS-polimeráz működését. Ennek elkerülése érdekében speciális proteinek kötődnek hozzá, amelyek meggátolják a másodlagos hurkok kialakulását a második szál elkészültéig.[21] Az egyszálú DNS-molekulát kapocsproteinek is körülveszik, amelyek belső üregében a lánc kényelmesen tud siklani és amelyekbe a DNS-polimeráz bele tud kapaszkodni, felgyorsítva a replikációt. Amikor a polimeráz eléri a templát végét vagy kettős szálat észlel maga előtt, a kapocs egy konformációs változás következtében leválik.[2]:274-5
A replikációs villán összegyűlt különböző funkciójú enzimek és struktúrproteinek alkotják a repliszómát. Ennek fontosabb alkotóelemei a következők:[22]
| Enzim | Szerepe a replikációban |
|---|---|
| Helikáz | Szétcsavarja a DNS kettős hélixének szálait a replikációs villánál |
| DNS-polimeráz | Az egyszálú DNS nukleotidsorrendje alapján 5'-3' irányban második szálat szintetizál. Ezenkívül hibaellenőrzést és -javítást is végez. A sejten belül többféle polimeráz létezik, mindegyik a maga külön feladatával |
| DNS-kapocs | Az a protein, amely megakadályozza a DNS-polimeráz leválását a DNS-ről |
| Egyszálú DNS-kötő fehérjék | A replikációs villa egyszálú DNS-hez kötve megakadályozza a kettős hélix és a másodlagos szerkezetek újraformálódását és a szálak térbeli eltávolításával gyorsítják a replikáció sebességét |
| Topoizomeráz | Megszünteti a kettős hélix másodlagosan felcsavart szerkezetét |
| DNS-giráz | Más néven topoizomeráz II. Enyhíti a torziós feszültséget a DNS-hélixben |
| DNS-ligáz | Összeköti a DNS-szálak végeit (például az Okazaki-fragmentumokat). |
| Primáz | A szintézis elkezdéséhez szolgáltat primert a polimeráz számára |
| Telomeráz | Az eukarióta kromoszómák végén található telomerekhez ad ismétlődő rövid szekvenciákat, ezáltal a sokszor osztódó őssejtek élettartamát meghosszabbítja[23] |
Termináció
[szerkesztés]Az eukarióta kromoszómán több ponton kezdődik a másolás, majd amikor a replikációs villa eléri a következő szakasz kezdetét, a polimeráz különösebb szabályozás nélkül leválik a kettős hélixről. A lineáris kromoszómák legvégét azonban nem tudják elérni és a másolást annak közelében, az ismétlődő szakaszokat tartalmazó telomer régióban abbahagyják. Emiatt az új szálak mindig rövidebbek valamivel a kiindulási DNS-szálnál. A testi sejtek a DNS-vesztés miatt csak bizonyos számú osztódást képesek elvégezni, ez az ún. Hayflick-korlát. Az ivarsejtekben a telomeráz enzim újabb rövid, ismétlődő szakaszokat illeszt a kromoszóma végére, így kerülik meg a korlátot. A telomeráz mutáció következtében testi sejtekben is aktiválódhat, ami könnyen tumor kialakulásához vezethet, sőt a rosszindulatú rákos elváltozás egyik előfeltétele.
A baktériumok kör alakú kromoszómáin a másolás akkor ér véget, amikor az origóval ellentétes oldalon a két replikációs villa találkozik. E. coli-ban ezen a helyen egy terminációs szekvencia található; ehhez a Tus-protein köt, amely meggátolja a helikáz működését, így a villák mindig a terminációs régióban találkoznak.[24]
Szabályozás
[szerkesztés]
Az eukarióták esetében a DNS-replikáció a sejtciklushoz kötött. A sejt növekedése és osztódása során különböző fázisokon megy át; a DNS másolása az S (szintézis) fázisban zajlik le. A sejtciklus előrehaladása és a fázisváltás ún. ellenőrző pontok révén történik, ezeket a ciklin és ciklindependens kináz proteinek szabályozzák.[25]
A DNS-replikációja (és az azt követő osztódás) a G1/S ellenőrzőpont állapotától függ. Azok a sejtek, amelyek megállnak ennél a pontnál G0 fázisban maradnak és nem másolják DNS-üket.
A mitokondriumok és kloroplasztiszok osztódása és DNS-másolása nem függ a sejtciklustól.
A baktériumok többsége nem meghatározott szakaszokra oszló sejtciklus során osztódik és folyamatosan másolhatja a DNS-ét. Bőséges táplálék és gyors növekedés esetén az egymás követő DNS-replikációk miatt több genom is felhalmozódhat a sejtben.[26] A legjobban ismert baktériumban, az E. coli-ban a DNS másolását több mechanizmus is szabályozza, mint például az hemimetilált origó (az egyik DNS-szálhoz való metilcsoport-kapcsolás), az ATP/ADP arány vagy a DnaA protein mennyisége. Valamennyi az iniciátorok origóhoz való hozzáférését gátolja.
Az E. coli vírusgátló restrikciós rendszere metilálja a saját GATC nukleotidszekvenciákat (mindkét szálon, lévén a GATC palindrom szekvencia). A replikáció után értelemszerűen csak a régi szál metilált, és ezt a hemi-(félig)metilált szakaszt felismeri a SeqA protein, amely hozzáköt és megakadályozza az újabb replikációt. Az iniciációt végző DnaA önmagában is nehezebben köti a hemimetilált DNS-t.[27]
Bőséges táplálék esetén az ATP szintje megemelkedik és ha a sejt bizonyos méretet elért, megindítja az osztódást megelőző DNS-másolást. ATP és az ADP egymással verseng a DnaA egyik kötőhelyéért és a létrejövő DnaA-ATP komplex képes iniciálni a replikációt. A DnaA fehérjemolekulák száma is limitáló lehet; minden replikáció után újabb origók, újabb kötőhelyek jönnek létre a számára és a kritikus mennyiség elérésére újabb DnaA proteinek szintézisére van szükség.
A polimeráz-láncreakció
[szerkesztés]Bár a sejtekben a DNS-replikáció sok enzim koordinált és szabályozott munkáját igénylő folyamat, leegyszerűsített formában kémcsőben is gyorsan végbemegy. Ezt használják ki a polimeráz-láncreakció során. A kiindulási DNS-hez kész primereket (rövid, egyszálú DNS-szakaszokat, amelyek felismerik a templát bizonyos szakaszait és hozzákötődnek), nukleozid-trifoszfátokat és hőálló DNS-polimerázt adnak. A helikázokat magas hőmérséklettel pótolják, amelyen a DNS két szála elválik egymástól. Miután hagyták a polimerázt dolgozni egy ideig, a reakcióelegyet újból felmelegítik és szétválasztják egymástól az újonnan készült szálakat is, amelyek a lehűtés után maguk is primerkötőhellyé válnak. Minden ciklusban megduplázódik a primerek által közrefogott DNS-szekvencia és néhány tíz ciklus után a nagyon kis mennyiségben jelen lévő DNS-szakasz (például egy kórokozó vagy igazságügyi orvostani minta) könnyen kimutathatóvá válik.[28]
Jegyzetek
[szerkesztés]- ↑ Imperfect DNA replication results in mutations. Berg JM, Tymoczko JL, Stryer L, Clarke ND. Chapter 27: DNA Replication, Recombination, and Repair, Biochemistry. W.H. Freeman and Company (2002). ISBN 0-7167-3051-0
- ↑ a b Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P. Chapter 5: DNA Replication, Repair, and Recombination, Molecular Biology of the Cell. Garland Science (2002). ISBN 0-8153-3218-1
- ↑ a b Berg JM, Tymoczko JL, Stryer L, Clarke ND. Chapter 27, Section 4: DNA Replication of Both Strands Proceeds Rapidly from Specific Start Sites, Biochemistry. W.H. Freeman and Company (2002). ISBN 0-7167-3051-0
- ↑ Alberts, B., et al., Molecular Biology of the Cell, Garland Science, 4th ed., 2002, pp. 238–240 ISBN 0-8153-3218-1
- ↑ Allison, Lizabeth A. Fundamental Molecular Biology. Blackwell Publishing. 2007. p.112 ISBN 978-1-4051-0379-4
- ↑ Berg JM, Tymoczko JL, Stryer L, Clarke ND. Biochemistry. W.H. Freeman and Company (2002). ISBN 0-7167-3051-0 Chapter 27, Section 2: DNA Polymerases Require a Template and a Primer
- ↑ a b c McCulloch SD, Kunkel TA (2008. január 1.). „The fidelity of DNA synthesis by eukaryotic replicative and translesion synthesis polymerases”. Cell Research 18 (1), 148–61. o. DOI:10.1038/cr.2008.4. PMID 18166979. PMC 3639319.
- ↑ McCarthy D, Minner C, Bernstein H, Bernstein C (1976). „DNA elongation rates and growing point distributions of wild-type phage T4 and a DNA-delay amber mutant”. J Mol Biol 106 (4), 963–81. o. DOI:10.1016/0022-2836(76)90346-6. PMID 789903.
- ↑ Drake JW (1970) The Molecular Basis of Mutation. Holden-Day, San Francisco ISBN 0816224501 ISBN 978-0816224500
- ↑ Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P. Molecular Biology of the Cell. Garland Science (2002). ISBN 0-8153-3218-1 Chapter 5: DNA Replication Mechanisms
- ↑ Weigel C, Schmidt A, Rückert B, Lurz R, Messer W (1997. november 1.). „DnaA protein binding to individual DnaA boxes in the Escherichia coli replication origin, oriC”. The EMBO Journal 16 (21), 6574–83. o. DOI:10.1093/emboj/16.21.6574. PMID 9351837. PMC 1170261.
- ↑ Lodish H, Berk A, Zipursky LS, Matsudaira P, Baltimore D, Darnell J. Molecular Cell Biology. W. H. Freeman and Company (2000). ISBN 0-7167-3136-312.1. General Features of Chromosomal Replication: Three Common Features of Replication Origins
- ↑ (2001. július 1.) „DNA Primases”. Annual Review of Biochemistry 70, 39–80. o. DOI:10.1146/annurev.biochem.70.1.39. PMID 11395402.
- ↑ Huberman JA, Riggs AD (1968). „On the mechanism of DNA replication in mammalian chromosomes”. J Mol Biol 32 (2), 327–341. o. DOI:10.1016/0022-2836(68)90013-2. PMID 5689363.
- ↑ Pursell, Z.F. (2007). „Yeast DNA Polymerase ε Participates in Leading-Strand DNA Replication”. Science 317 (5834), 127–130. o. DOI:10.1126/science.1144067. PMID 17615360. PMC 2233713.
- ↑ Kunkel, Thomas (2011. október 1.). „Balancing eukaryotic replication asymmetry with replication fidelity”. Current Opinions in Chemical Biology 15 (5), 620–626. o. DOI:10.1016/j.cbpa.2011.07.025.
- ↑ Hansen, Barbara. Biochemistry and Medical Genetics: Lecture Notes. Kaplan Medical, 21. o. (2011)
- ↑ Elizabeth R. Barry; Stephen D. Bell (2006. december 1.). „DNA Replication in the Archaea”. Microbiology and Molecular Biology Reviews 70 (4), 876–887. o. DOI:10.1128/MMBR.00029-06. PMID 17158702. PMC 1698513.
- ↑ Distinguishing the pathways of primer removal during Eukaryotic Okazaki fragment maturation Contributor Author Rossi, Marie Louise. Date Accessioned: 2009-02-23T17:05:09Z. Date Available: 2009-02-23T17:05:09Z. Date Issued: 2009-02-23T17:05:09Z. Identifier Uri: http://hdl.handle.net/1802/6537. Description: Dr. Robert A. Bambara, Faculty Advisor. Thesis (PhD) – School of Medicine and Dentistry, University of Rochester. UR only until January 2010. UR only until January 2010.
- ↑ Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P. Molecular Biology of the Cell. Garland Science (2002). ISBN 0-8153-3218-1 DNA Replication Mechanisms: DNA Topoisomerases Prevent DNA Tangling During Replication
- ↑ Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P. Molecular Biology of the Cell. Garland Science (2002). ISBN 0-8153-3218-1 DNA Replication Mechanisms: Special Proteins Help to Open Up the DNA Double Helix in Front of the Replication Fork
- ↑ Griffiths A.J.F., Wessler S.R., Lewontin R.C., Carroll S.B.. Introduction to Genetic Analysis. W. H. Freeman and Company (2008). ISBN 0-7167-6887-9[Chapter 7: DNA: Structure and Replication. pg 283–290]
- ↑ Will the Hayflick limit keep us from living forever?. Howstuffworks . (Hozzáférés: 2015. január 20.)
- ↑ TA Brown. Genomes. BIOS Scientific Publishers (2002). ISBN 1-85996-228-913.2.3. Termination of replication
- ↑ Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P. Molecular Biology of the Cell. Garland Science (2002). ISBN 0-8153-3218-1 Intracellular Control of Cell-Cycle Events: S-Phase Cyclin-Cdk Complexes (S-Cdks) Initiate DNA Replication Once Per Cycle
- ↑ Tobiason DM, Seifert HS (2006). „The Obligate Human Pathogen, Neisseria gonorrhoeae, Is Polyploid”. PLoS Biology 4 (6), e185. o. DOI:10.1371/journal.pbio.0040185. PMID 16719561. PMC 1470461.
- ↑ Slater S, Wold S, Lu M, Boye E, Skarstad K, Kleckner N (1995. szeptember 1.). „E. coli SeqA protein binds oriC in two different methyl-modulated reactions appropriate to its roles in DNA replication initiation and origin sequestration”. Cell 82 (6), 927–36. o. DOI:10.1016/0092-8674(95)90272-4. PMID 7553853.
- ↑ Saiki, RK (1988). „Primer-directed enzymatic amplification of DNA with a thermostable DNA polymerase”. Science 239 (4839), 487–91. o. [2008. december 19-i dátummal az eredetiből archiválva]. DOI:10.1126/science.2448875. PMID 2448875. (Hozzáférés: 2015. június 9.)
Fordítás
[szerkesztés]- Ez a szócikk részben vagy egészben a DNA Replication című angol Wikipédia-szócikk ezen változatának fordításán alapul. Az eredeti cikk szerkesztőit annak laptörténete sorolja fel. Ez a jelzés csupán a megfogalmazás eredetét és a szerzői jogokat jelzi, nem szolgál a cikkben szereplő információk forrásmegjelöléseként.
